- Details
- Category: IPT
- Hits: 213
Bioinformatique
Comparaison de génomes & Analyse différentielle
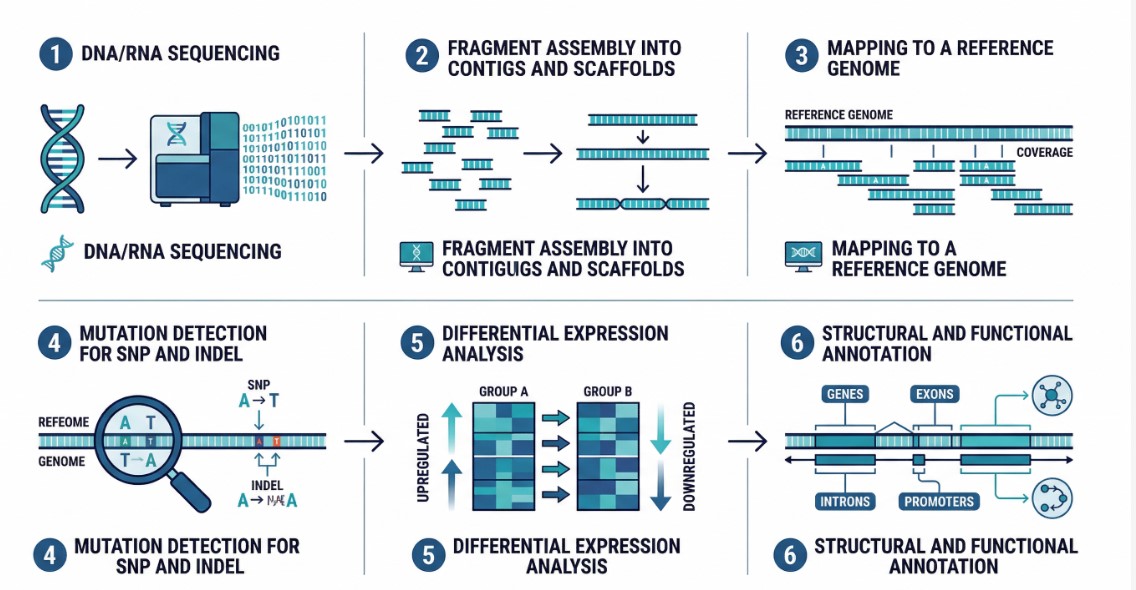
Comparaison de génomes et détection de mutations
Relier le phénotype aux données génomiques est un défi majeur. Nos solutions permettent de détecter les mutations et de comparer des génomes complets, pour identifier des gènes ou variations clés liées à un phénotype moléculaire ou cellulaire.
Applications :
- Identification de cibles thérapeutiques
- Sélection de souches spécifiques
- Découverte de nouveaux biomarqueurs
La détection de mutations (SNP, INDEL) repose sur le mapping des séquences sur un génome de référence, garantissant une comparaison fiable entre échantillons.
Analyse de l’expression génique
L’étude de l’expression des gènes révèle les mécanismes cellulaires et permet d’identifier des biomarqueurs d’intérêt. Grâce au RNA-Seq, nous comparons l’expression génétique :
- Entre tissus sains et pathologiques
- Sous différentes conditions (stress, nutrition, pollution…)
- À différents stades de développement
Avantages :
- Analyse complète du transcriptome, sans connaissances préalables
- Possibilité de générer un transcriptome de novo
- Identification de gènes et biomarqueurs clés
Analyse bioinformatique & Assemblage
Nos experts reconstituent des génomes et transcriptomes à partir de fragments de séquençage grâce à des algorithmes avancés :
- Assemblage de novo ou basé sur référence
- Mapping sur séquences de référence
- Annotation structurale et fonctionnelle
Cette approche permet d’identifier les variations génomiques et de comprendre leur rôle biologique.
Annotation – Comprendre le génome
L’annotation relie les séquences aux fonctions biologiques :
- Structurale : localisation des gènes et ORFs
- Fonctionnelle : comparaison avec des bases de données pour identifier motifs et fonctions biologiques
Pourquoi choisir IPT’omics ?
- Accompagnement complet, du design expérimental à l’analyse bioinformatique
- Protocoles optimisés pour fiabilité et reproductibilité
- Rapports clairs et synthétiques, mettant en évidence les différences clés